摘 要:苎麻是一种重要的纤维作物,纤维被用作纺织工业的原料。扩展蛋白具有诱导依赖pH的细胞壁伸长和压力松弛的特性。为了对苎麻基因组中expansin家族成员数量和类型进行鉴定,并研究在纤维细度不同的苎麻茎皮中扩展蛋白基因的表达情况,研究首先在芒麻中艺1号基因组数据库挖掘到24个扩展蛋白基因家族成员。通过生物信息学方法对其分子量、等电点、信号肽、亚细胞定位、motif及基因结构进行分析和预测。系统进化树结果显示:扩展蛋白包括α亚族成员17个、β亚族4个、α类亚族1个和β类亚族2个,共分为3类;expansin家族同一进化支蛋白结构域比较保守且有一个特有的motif。然后,利用苎麻茎皮扩展蛋白基因家族成员转录组表达分析和GRT-PCR验证,发现两个基因在两个纤维细度差异显著的品种及其5个不同生长期表达量差异显著。该结果有助于了解苎麻expansin家族的进化,为影响苎麻纤维发育和纤维细度相关基因及其功能的研究奠定基础。
关键词:苎麻;expansin家族;生物信息学分析;表达分析
扩展蛋白最早被鉴定为一种具有细胞壁松弛作用的蛋白,部分介导了植物细胞壁延伸和细胞生长。扩展蛋白主要分为两个蛋白家族,即α和β扩展蛋白亚族,他们不仅作用于细胞膨胀,还参与调节包括形态发生、果实软化、花粉管生长等多种植物生长过程[1]。蛋白功能被细胞壁酸性条件激活,在植物中存在一些反应机制会诱导细胞壁pH值发生变化而影响细胞的生长[2]。由于扩展蛋白对细胞壁具有独特的修饰作用,先后在棉花和苎麻关于纤维发育的研究中得到关注,已有研究发现3种编码扩展蛋白的基因在苎麻的上部茎皮上调表达[3-4]。一些家族成员基因在其他植物中的功能相继被证实,涉及促进生长、改善纤维品质和盐胁迫响应,例如水稻OsEXP4[5]、棉花GhEXPA8[6]和GbEXPATR[7]、小麦0sEXPB23[8]等。扩展蛋白在苎麻中的研究才刚刚起步,该家族基因具体的分子功能及其对纤维细胞的发育和纤维品质的影响尚不清楚。
在Swiss-Prot数据库中:水稻的56个编码扩展蛋白的基因,包括α亚族34个,β亚族19个;拟南芥36个编码扩展蛋白的基因包括α亚族25个和β亚族7个;玉米4个基因都于β亚族。苎麻中通过转录组序列拼接和同源基因克隆的方法发现了12个α亚族和4个β亚族,共16个编码扩展蛋白的基因[9]。然而,目前还未对节麻expansin家族成员的具体数目和类型进行全面鉴定。节麻基因组测序草图的顺利完成[10],使利用生物信息学在全基因组水平上分离和鉴定expansin家族成为可能。因此,本研究利用艺麻基因组数据库对芦麻expansin家族成员及其类型进一步鉴定与分析,旨在为芒麻纤维发育候选基因挖掘奠定基础。
1材料与方法
1.1苎麻expansin家族成员鉴定
在Pfam数据库下载扩展基因家族保守结构域数据文件(登录号分别为PF03330和PF01357),利用hmmer v3.0软件构建苎麻expansin家族专有的保守结构域隐马尔可夫模型文件,然后在苎麻基因组蛋白数据中搜索家族成员[11]。将家族蛋白氨基酸序列在HMMER网站(https://www.ebi.ac.uk/Tools/hmmer/search/phmmer)进行序列分析。
1.2理化性质分析和亚细胞定位
通过ExPASy网站(https://www.expasy.org/)中的Protparam程序分析蛋白质的分子量、等电点,利用Signal P-5.0预测蛋白的信号肽,采用pLoc-mPlant进行蛋白的亚细胞定位预测。
1.3扩展基因结构及蛋白序列分析
利用在线软件MEME(http://meme-suite.org/)对扩展蛋白保守结构域进行分析。最大motif数量设为20,其他参数为默认值。根据苎麻基因组的DNA序列和编码区序列,使用TBtools软件[12]分析和绘制基因家族成员的基因结构图。
1.4基因家族系统进化分析
利用分子进化分析软件MEGA7的Clustalw程序对鉴定的苎麻扩展蛋白氨基酸序列进行多重序列比对,采用邻接法(NJ,neighbor-joining)构建系统发育树。在Swiss-Prot数据库下载水稻和拟南芥的expansin家族的蛋白氨基酸序列,与苎麻的蛋白氨基酸序列进行比对,默认参数,bootstrap值设为500,构建NJ进化树。
1.5表达分析
依据本课题组已经完成的苎麻转录组测序结果,即2个纤维细度差异大的品种,编号为2-25(纤维细度1312m/g)和3-4(2788m/g),发芽2周(T1),4周(T2),6周(T3),8周(T4)、10周(T5)5个不同纤维发育时期茎皮中各基因的FPKM值[13-14],分析其5个发育时期的expansin家族基因表达模式。利用与转录组相同的样品材料(液氮冷冻,-80℃保存),提取苎麻茎皮总RNA,RNA提取方法和模板cDNA的合成均按照试剂盒操作手册。TaKaRa MiniBEST Universal RNA Extraction Kit 用于茎皮总RNA提取,Thermo Scientific RevertAid first-strand cDNA synthesis kit (Thermo Scientiic,Vilnius,Lithuania) 用于cDNA合成,合成20μL体系cDNA,用ddH2O稀释一倍后备用。根据扩展蛋白基因家族表达差异的结果在Primer 5 设计相关基因的特异性引物,以苎麻18S rRNA为内参基因,于Bio-Rad iQ5 Real-Time PCR System(Bio-Rad,CA,USA)分析仪上进行qRT-PCR分析,25μL qPCR体系,即1μL cDNA,12.5μL 2xSYBR qPCR Mix (北京艾德莱生物公司),各1μL上下游引物(10μmol/L)和10.5μL ddH2O,程序为95℃2min、95℃15s和55℃30s,40个循环,每个样品设3个重复,并按照2-△△CT的方法计算基因的相对表达量[15]。利用GraphPad Prism8软件的Holm-Sidak方法对表达量进行t测验,以比较基因在品种间和时期间的差异显著性。
2结果与分析
2.1基因家族成员的鉴定及理化性质分析
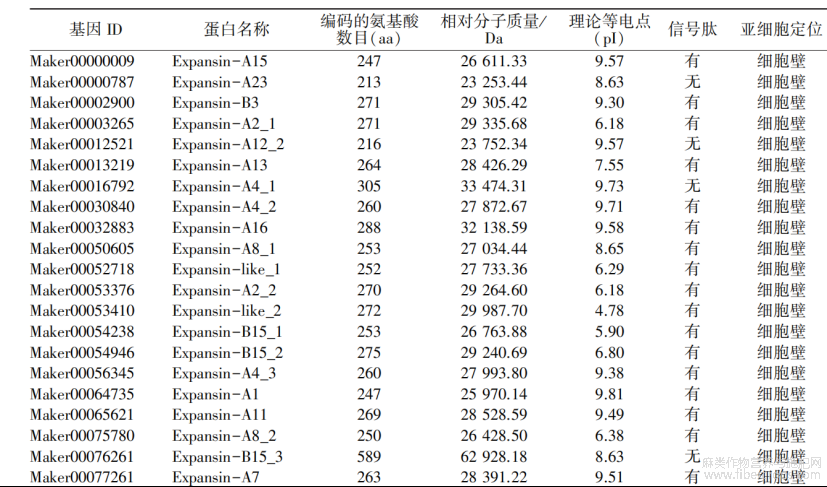
通过全基因组基因家族成员挖掘,去掉结构和功能冗余的2个候选序列,共获得了27个expansin基因候选序列。在Pfam数据库对这些序列进行结构域注释,发现24个具有家族保守结构域的DPBB_1和Pollen_allerg_1,3个缺失第二个结构域的候选序列。对此24个具有完整结构域基因的命名沿用苎麻基因组蛋白数据库注释。
比较和分析24个共麻扩展蛋白序列的理化性质(表1),基酸数目213aa(Expansin-A23)~589aa(Expansin-B15_3),分子量23253.44Da(Expansin-A23)~62 928.18Da(Expansin-B15_3),等电点4.78(Expansin-like_2)~9.96(Expansin-A12_1)。预测发现5个蛋白序列没有信号肤,分别为Expansin-A23、Expansin-A12_2、Expansin-A4_1、Expansin-B15_3、Expansin-A12_1。亚细胞定位结果显示24个苎麻扩展蛋白均位于细胞壁。
表1苎麻扩展蛋白基本理化性质
2.2基因家族的基因结构及蛋白质基序预测
苎麻expansin家族成员外显子数目为2~9个,内含子数目为1~8个。根据MEME分析结果,选择其中E-value最低为8.4e-003的17个保守基序作图(图1)。同一进化支蛋白的结构域均保守且每个基因亚族蛋白含特有的保守基序(motif),α亚族蛋白特有motif3,β亚族特有motif8,EXPL支(EXPLA亚族和EXPLB亚族)特有motif15。
图1扩展家族蛋白序列保守基序和基因结构与3个特有保守基序
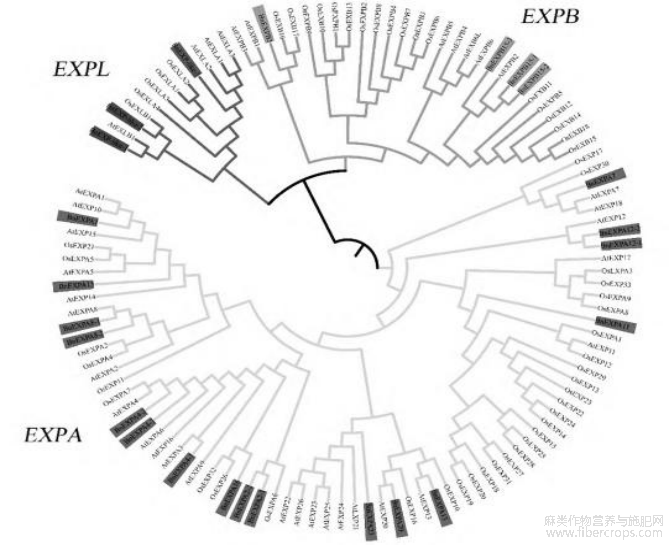
2.3苎麻expansin家族的系统进化分析
在Swiss-Prot数据库下载水稻和拟南芥的expansin家族的蛋白氨基酸序列,分别为36和56条,与24条苎麻蛋白氨基酸序列一起构建进化树(图2)。expansin家族包括EXPA、EXPB、EXPLA、EXPLB等4个亚族,在进化树中可分为EXPA、EXPB、EXPL3大类。EXPA类包含苎麻expansin家族的17个基因(α亚族),EXPB类包含4个基因(β亚族),EXPL类有3个基因(1个α类亚族和2个β类亚族)。
图2苎麻expansin家族进化树
2.4基因家族成员的表达分析
5个发育时期的expansin家族基因表达模式如图3所示9个基因在两个品种间存在明显的差异表达情况,其中BnEXPA16、BnEXP-like-3和BnEXPA20仅在品种3-4的T3、T4及T5期上调表达,BnEXP-like-1和BnEXPA7仅在品种2-25的T4期上调表达,BnEXPA8-2、BnEXPB3、BnEXPA23和BnEXPA11仅在品种2-25的T2期上调表达。两个苎麻品种5个生长期内,在T1和T2期都上调表达的有BnEXPA2-1、BnEXPA2-2、BnEXP-like-2、BnEXPA8-1、BnEXPA12-1、BnEXPA8-2、BnEXPA1、BnEXPA15、BnEXPA4-1、BnEXPA13。在T3、T4和T5期都上调表达的有BnEXPB15-1、BnEXPB15-2和BnEXPB15-3。
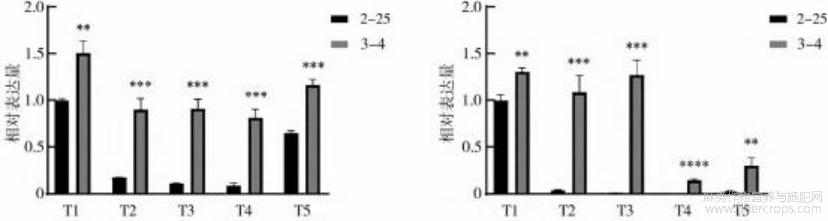
根据转录组数据分析结果和相关差异表达基因的功能分析,选择BnEXP-like-3和BnEXPB15-2这两个基因做进一步分析(特异性引物序列见表2),荧光定量PCR结果(图4)显示,5个时期苎麻茎皮中两个基因的表达量呈现显著差异(p<0.01),两个基因在品种3-4表达量明显高于2-25的表达量。
图3苎麻expansin家族基因表达量热图
表2expansin家族基因特异qRT-PCR引物(5’→3’)
注:“∗”表示p<0.05的显著差异性,“∗∗”表示p<0.01,“∗∗∗”表示p<0.001,……。
图4BnEXP-like-3(左)和BnEXPB15-2(右)在两个苎麻品种茎皮5个时期的相对表达量
3讨论与结论
苎麻中鉴定出的4种扩展蛋白亚族的蛋白,包括α亚族17个、β亚族4个、α类亚族1个和β类亚族2个。蛋白质的氨基酸序列分析表明,可依据其特有的保守基序区分不同亚族的扩展蛋白,苎麻expansin家族α亚族蛋白特有motif3,β亚族特有motif8,α类亚族和β类亚族共特有motif15。表达分析结果显示,expansin家族成员在不同品种和时期存在表达差异,且BnEXP-like-3与BnEXPB15-2两个基因在品种3-4中冬人时期的相对表达量均高于2-25。目前被报道与纤维发育相关的扩展蛋白基本属于如EXP1、EXPA2、EXPA8等所在的成员数量占有优势的a亚族[3-4,6-7],而鲜有α类亚族和β亚族的成员。另外,有研究发现,苎麻纤维细度还受光照、湿度、温度等生态环境因素的影响[16]。本研究首次发现在两个在纤维细度不同的两个品种间呈表达差异的BnEXP-like-3与BnEXPB15-2,其所在亚族的蛋白被报道与植物抗逆性相关,如启动子序列存在脱落酸、生长素、水杨酸等激素诱导元件和对干旱、高温等非生物胁迫的响应元件的OfEXLA1[17]及被证实由磷酸盐饥饿诱导且能够提高大豆磷效率的GmEXPB2[18]。因此BnEXP-like-3和BnEXPB15-2是否具有通过对苎麻生长环境响应而影响纤维细度的功能值得深入探讨。
棉花中发现了两个扩展蛋白基因,GbEXPA2通过增加结晶纤维素含量影响纤维细胞厚度,GbEXPATR是编码一个缺失Pollen_allerg_1结构域的蛋白基因,同属于扩展蛋白α亚族,过表达GbEXPATR纤维会产生更长、更结实的薄壁纤维[7]。在本研究中也发现了3个缺失第二结构域的蛋白,其中两个有信号肽,但与扩展蛋白家族各个亚族的蛋白相似性不高,其功能有待进一步研究。
参考文献:
[1]LEE Y,CHOI D,KENDE H.Expansins:ever-expanding numbers and functions[J].Current Opinion in Plant Biology,2001,4(6):527-532.
[2] COSCROVE D J.Growth of the plant cell wall[J].Nature Reviews Molecular Cell Biology,2005,6(11):850-861.
[3] RUAN Y L,ILEWELLYN D J,FURBANK R T.The control of single-celled cotton fiber elongation by developmentally reversible gating of plasmodesmata and coordinated expression of sucrose and K+ transporters and expansin[J].Plant Cell,2001,13(1):47-60.
[4] CHEN J,PEL Z H,DALI L J,et al,Transcriptome profiling using pyrosequencing shows genes associated with bast fiber development in ramie(Boehmeria nwea L.)[J].BMC Genomics,2014,15:919.
[5] CHOI D S,LEE Y,CHO H T,et al.Regulation of expansin gene expression affects growth and development in transgenic rice plants[J].Plant Cell,2003,15(6):1386-1398.
[6] BAJWA K S,SHAHID A A,RA0 A Q,et al.Stable transformation and expression of GhEXPA8 fiber expansin gene to improve fiber length and micronaire value in cotton[J].Frontiers in Plant Science,2015,6.838.
[7] LI Y,TU L L,PETTOLINO F A,et al.GbEXPATR,a species-specifc expansin,enhances coton fibere elongation through cell wall restructuring[J].Plant Biotechnology Journal,2016,14(3).951-963.
[8] HAN Y Y,LI A X,L1 F,et al.Characterization of a wheat(TrticumaestitumL.)expansin gene,TaEXPB23,involved in the abiotic stress response and phytohormone regulation[J].Plant Physiology and Biochemistry,2012,54.49-58
[9] 陈杰.麻纤维发育相关转录组测序及expansin家族功能分析[D].武汉:华中农业大学,2017.
[10]LUAN M B,JIAN J B,CHEN P,et al.Draft genome sequence of ramie,Boehmeria nitea(L.)Gaudich(J].Molecular Ecology Resources,2018,18(3):639-645.
[11]LOZANO R,HAMBLIN M T,PROCHNIK S,et al.Identification and distribution of the NBS-LRR gene family in the Cassava genome[J].BMC Genomics,2015,16:360.
[12]CHENC J,CHEN H,ZHANC Y,et al.TBtools:an interative toolkit developed for interactive analyses of big biological data [J]Molecular Plant,2020,13(8):1194-1202.
[13]CHEN K M,MING Y,LUAN M B,et al.The chromosome-level assembly of ramie(Boehmeria Nivea L.)genome provides insights into molecular regulation of fiber fineness[L].Journal of Natural Fibers,2023,20(1):2168819.
[14]黄坤勇.苎麻纤维细度全基因组关联分析及候选基因筛选[D].北京:中国农业科学院,2020.
[15]谭龙涛.苎麻氮代谢高效基因型筛选及表达分析[D].北京:中国农业科学院,2015.
[16]湖南省苎麻优质高产的气象条件研究协作组,刘淑梅.苎麻优质高产的气象生态条件试验研究[J].中国麻作,1991,2:13-20.
[17]高晓月,董彬,张超,等.桂花扩展蛋白基因OfEXPA2、OfEXPA4和OfEXIA1启动子克隆及活性分析[J].浙江大学学报(农业与生命科学版),2019、45(1):23-29.
[18]ZHOU J,XIE J N,LIAO H,et al.Overexpression of beta-expansin gene GmEXPB2 improves phosphorus efficiency in soybean[J].Physiologia Plantarum,2014,150(2):194-204.
文章摘自:石亚亮,钟意成,黄坤勇等.苎麻expansin家族成员鉴定与表达分析[J].中国麻业科学,2023,45(04):145-151.